Le cachalot pygmée vit aussi en Méditerranée, la fascinante découverte italienne grâce à l'ADN environnemental
Le cachalot pygmée vit également en Méditerranée : un groupe de recherche dirigé par l'Université de Milan-Bicocca, dans le cadre d'un projet européen coordonné par l'ISPRA, a démontré l'existence de l'espèce dans notre mer grâce à l'ADN environnemental. Mais les observations pourraient être difficiles
Le cachalot pygmée vit également en Méditerranée, une espèce que l’on pensait absente de nos mers. Un groupe de recherche dirigé parUniversité de Milan-Bicoccadans le cadre du projet Life CONCEPTU MARIS coordonné par ISPRA, a démontré l'existence de l'espèce dans notre mer grâce à l'ADN environnemental. Mais les observations pourraient être difficiles.
Qu'est-ce que l'ADN environnemental et pourquoi est-il un outil de recherche
Comme l'explique l'ARPA Friuli Venezia-Giulia, e-DNA, qui signifie «ADN environnemental» (« ADN environnemental »), est l'ensemble des molécules d'ADN présentes dans les matrices environnementales telles que l'eau, les sédiments et l'air. En fait, tout le monde laisse des traces : tous les organismes, en pratique. ils rejettent l'ADN dans l'environnement sous forme de mucus, d'excréments, de cellules cutanées et de gamètes.
L'e-ADN peut être utilisé comme outil de recherche car il est possible de comparer des séquences d'ADN entre elles, afin de trouver la plus similaire afin de déterminer à quelle espèce appartient l'organisme étudié.
'; var fallbackTriggered = faux ; var timeoutId = null ; function renderTaboolaFallback(reason) { if (fallbackTriggered) return ; fallbackTriggered = vrai ; si (timeoutId) { clearTimeout (timeoutId); timeoutId = nul ; } console.log('(ADV) Rendu de secours Taboola. Raison :', raison); root.innerHTML = ''; window._taboola.push({ mode : 'thumbnails-300×250', conteneur : taboolaDivId, placement : 'Widget milieu d'article 300×250', target_type : 'mix' }); // Si votre intégration Taboola le nécessite, décommentez : // window._taboola.push({ flush: true }); } googletag.cmd.push(function () { console.log('(ADV) GPT init', gptDivId); var gptSlot = googletag .defineSlot('/22142119198/greenme.it/roller', (300, 250), gptDivId) .addService(googletag.pubads()); googletag.pubads (). event.lineItemId }); if (fallbackTriggered) return ; if (event.isEmpty) { renderTaboolaFallback('gpt-empty'); googletag.enableServices();
En général – cela est connu depuis un certain temps – plus les espèces sont proches sur le plan évolutif, plus ces séquences sont similaires. Mais les techniques modernes de séquençage de l’ADN sont capables de détecter même de très petites différences dans des nucléotides uniques et il est donc presque toujours possible d’associer une séquence à l’espèce concernée.
Comment la découverte s'est produite
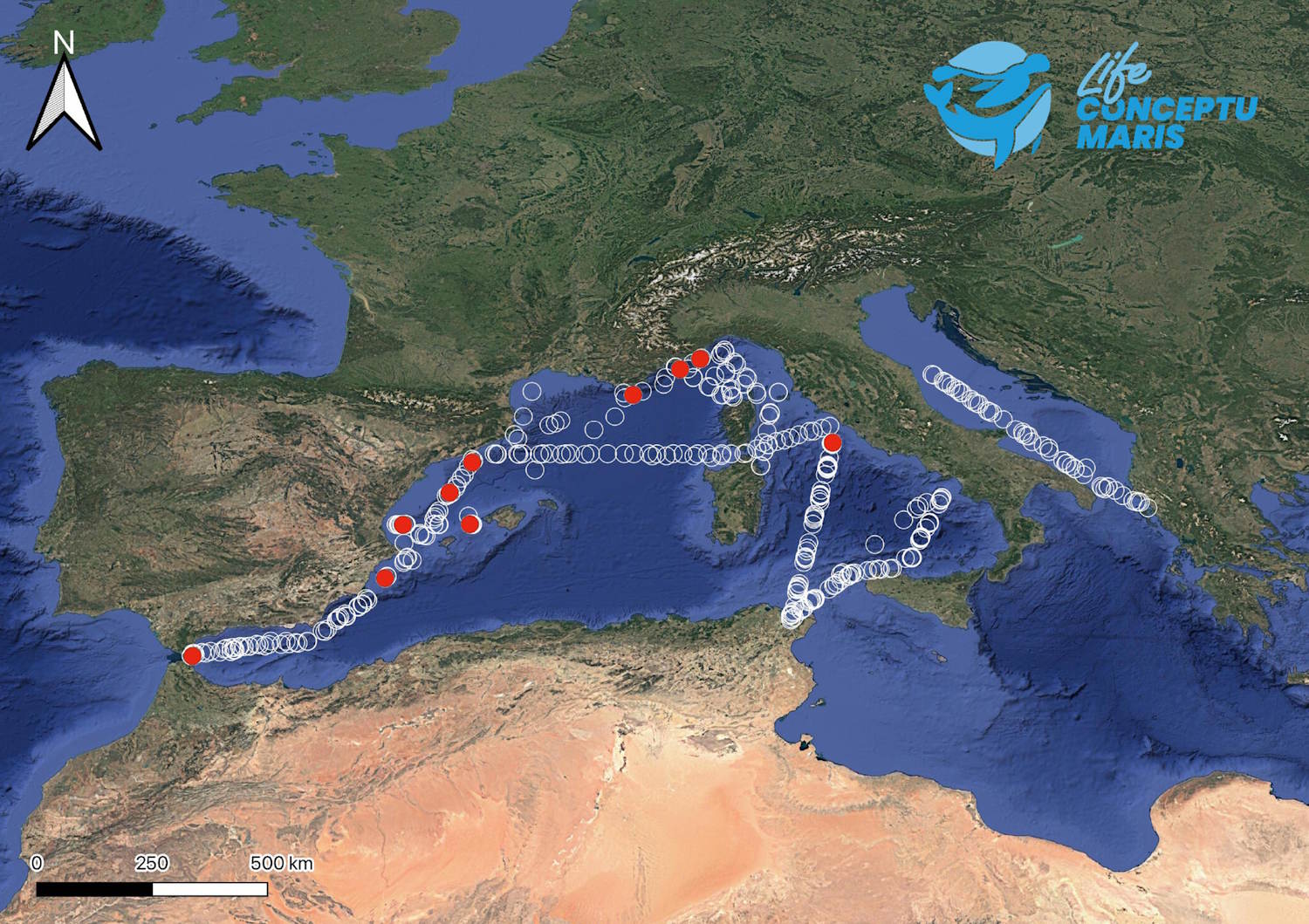

C’est précisément ainsi que les chercheurs ont découvert que le cachalot pygmée vit également en Méditerranée : la recherche s’est notamment déroulée en trois étapes :
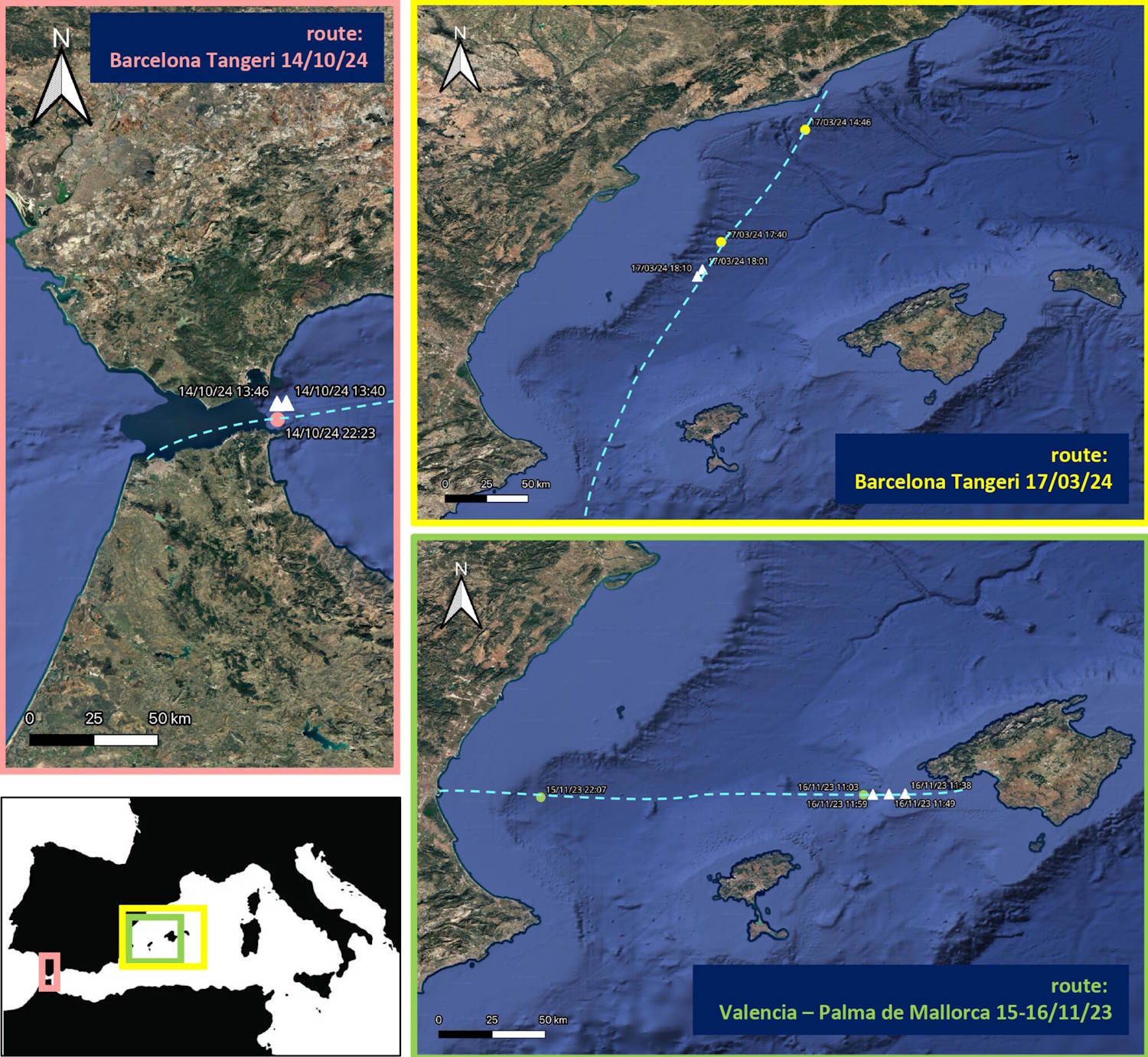
- Collecte –> Les chercheurs ont prélevé des échantillons d'eau de mer sur des ferries commerciaux en cours de route : au total, 12 litres d'eau ont été collectés pour chacun des 393 points de prélèvement répartis dans le centre-ouest de la Méditerranée.
- Filtration –> L'eau était immédiatement filtrée à bord des navires en la faisant passer à travers des membranes spéciales dotées de minuscules pores : cette étape est essentielle pour capter toute la matière biologique en suspension contenant des fragments d'ADN.
- Analyse -> En laboratoire, l'ADN a été extrait des filtres ; Par la suite, grâce à des techniques de séquençage avancées, des milliers de séquences d’ADN ont été obtenues à partir de chaque échantillon, puis comparées à de vastes bases de données de référence pour identifier à quelle espèce elles appartiennent.
Ce que les scientifiques ont découvert
L'attribution génétique est sans équivoque : les scientifiques ont retrouvé l'ADN de la cogia de De Blainville (nom scientifique Breviceps de Kogia), également appelé cachalot pygmée, dans 10 échantillons attribuables à au moins 5 événements d'occurrence distincts, répartis entre la mer Tyrrhénienne et le détroit de Gibraltar. Cela montre que l’espèce vit également dans nos mers.
Le cachalot pygmée est très difficile à observer, car il est notoirement très insaisissable en surface : cette caractéristique a toujours empêché son identification. Cependant, dans les mêmes domaines et aux mêmes époques où l'ADN de K. brevicepsles observateurs à bord des ferries avaient signalé un nombre disproportionné d’observations de « petits cétacés non identifiés ». On pense qu’il s’agissait bien de cachalots pygmées, mais que, compte tenu de leur rareté en surface, personne n’avait jamais pu les reconnaître.
L'ADN environnemental nous a permis de « voir » une espèce qui était toujours restée cachée, démontrant qu'il y a encore tant de choses à découvrir même dans les mers que nous pensions bien connaître – explique Elena Valsecchi, qui a dirigé la recherche – Cette étude ajoute non seulement un nouveau mammifère marin fascinant à la liste de la faune méditerranéenne, mais souligne également le pouvoir de ces outils pour révéler la biodiversité cachée de nos océans. Regarder la mer avec ces « yeux moléculaires » sera fondamental pour guider les futures stratégies de conservation et également pour protéger les formes de vie que nous ne connaissons pas encore.

De plus, la recherche a également mis en évidence une vaste répartition géographique et temporelle des détections, ainsi que la présence de différents profils génétiques (haplotypes) : pour cette raison, les scientifiques estiment qu'ils ne sont pas confrontés à des individus isolés provenant de l'Atlantique, mais à une population stable et enracinée du type de De Blainville en Méditerranée.
Entre autres choses, ce qui a été découvert est un haplotype mitochondrial unique, différent de ceux des spécimens atlantiques proches de Gibraltar (bien qu'elle soit plus similaire, bien que différente, à celles trouvées en Écosse ou aux îles Canaries), ce qui pourrait indiquer l'existence d'une sous-population restée longtemps isolée, avec une longue histoire évolutive au sein du bassin.
La découverte n'est pas qu'une curiosité scientifique : elle justifie en effet la demande d'inscription officielle de la cogia de De Blainville (Breviceps de Kogia) dans les listes de protection internationales pour la Méditerranée, comme l'accord ACCOBAMS, pour garantir sa protection.
L'ouvrage a été publié le Examen des mammifères.
Sources : Université de Milan-Bicocca / Mammal Review / Vie CONCEPTU MARIS / Vie CONCEPTU MARIS/Youtube / Vie CONCEPTU MARIS/Facebook







